Correction MAP (CMAP)とは
古典力場にはクセがあり,生体分子系では特定の2次構造が出やすいなどの欠点があります.古典力場の一つであるCHARMM力場もその特徴を持っていましたが,そのバイアスを軽減するために,Correction MAP(CMAP)をCHARMMは導入しています[1].
そもそも,なぜ特定の2次構造が出やすくなってしまっているのでしょうか?それは2面角のポテンシャルエネルギーの記述方法にあると考えられます.CHARMMやAmber力場における2面角のエネルギーは
で表されます.ここで,は全ての2面角の集合,は2面角の力の定数,はそれぞれ,周期性(整数値)と位相です.このように2面角のエネルギーはのみに依存する形をとります.しかし,蛋白質の主鎖の2面角は互いに影響し合うので,2面角のエネルギーは2つの2面角に依存した形で表す方が自然です.
そこで,補正エネルギーを導入することで(1)を修正することを考えます.この補正エネルギーは2面角の特徴を捉えるためのモデル系(e.g., alanine dipeptide)に対して量子化学計算を行うことで取得します.
2面角を15°づつ動かし各々の角度において量子化学計算を行います.すると,2424個のグリッドセルに対して量子化学計算から取得したエネルギーを割り当てることができます.
2面角を15°づつ動かした各々の構造に対して,結合,角度,2面角から得られるエネルギーを計算し,
を得ます.(結合と角度は平衡長,平衡角で固定した状態でポテンシャルエネルギーを計算しています.なので,の差はQMとMM で変わらないという仮定を置いています.)
これが補正エネルギーの生データです.これに対して,より滑らかな補正をするため,Bicubic補完を使用し,任意のに対する,補正エネルギーを得ます.
Gromacsにおけるcmapの記述箇所の例
Gromacsのtopologyファイルを参照すると行cmaptypes以下にcmapの情報が書かれています.以下が例になります:
[ cmaptypes ]
; cmap parameters from
; cmap parameters from toppar_c36_jul22/metals/CHARMM_METAL/par_all22_prot_metals.inp
; cmap parameters from toppar_c36_jul22/metals/CHARMM_METAL/top_all22_prot_metals.inp
; cmap parameters from toppar_c36_jul22/par_all35_ethers.prm
; cmap parameters from toppar_c36_jul22/par_all36_carb.prm
; cmap parameters from toppar_c36_jul22/par_all36_cgenff.prm
; cmap parameters from toppar_c36_jul22/par_all36_lipid.prm
; cmap parameters from toppar_c36_jul22/par_all36_na.prm
; cmap parameters from toppar_c36_jul22/par_all36m_prot.prm
C NH1 CT1 C NH1 1 24 24\
0.54392000 3.22168000 4.05848000 5.23000000 8.87008000 11.38048000 8.74456000 7.48936000 3.26352000 -2.88696000\
4.18400000 -9.20480000 -20.20872000 -20.16688000 -20.54344000 -15.02056000 -11.58968000 -11.63152000 -10.25080000 -9.83240000\
-9.79056000 -6.35968000 -3.97480000 -0.16736000 -0.54392000 5.77392000 6.61072000 7.82408000 10.04160000 10.41816000\
10.20896000 8.07512000 4.56056000 2.67776000 1.08784000 -11.71520000 -16.77784000 -17.32176000 -14.30928000 -10.87840000\
-9.62320000 -6.27600000 -4.60240000 -3.59824000 -2.67776000 -0.87864000 -4.51872000 -4.68608000 0.33472000 5.94128000\
6.77808000 8.57720000 11.08760000 11.38048000 9.70688000 8.32616000 6.52704000 10.29264000 -0.96232000 -7.61488000\
-10.79472000 -12.59384000 -10.66920000 -7.90776000 -5.64840000 -3.05432000 0.29288000 -0.96232000 -3.22168000 -5.35552000\
-5.39736000 -3.43088000 3.89112000 6.35968000 9.37216000 10.66920000 13.01224000 12.21728000 10.29264000 9.16296000\
8.61904000 7.74040000 0.50208000 -4.93712000 -8.36800000 -9.53952000 -8.20064000 -5.60656000 -3.89112000 0.08368000\
1.29704000 -2.17568000 -4.81160000 -4.10032000 -2.38488000 -1.84096000 5.69024000 8.20064000 11.29680000 12.71936000\
15.48080000 14.89504000 11.04576000 11.58968000 11.38048000 6.81992000 2.97064000 -3.30536000 -8.87008000 -11.00392000\
-7.53120000 -1.79912000 -0.25104000 1.84096000 3.80744000 -2.30120000 -4.05848000 -3.59824000 -1.04600000 1.88280000\
8.57720000 10.62736000 11.79888000 12.92856000 14.10008000 14.85320000 12.84488000 12.13360000 12.38464000 8.87008000\
3.80744000 -3.43088000 -8.74456000 -9.37216000 -6.10864000 0.87864000 0.33472000 3.22168000 4.35136000 -0.50208000\
-1.33888000 -0.66944000 1.29704000 3.05432000 6.06680000 11.50600000 11.46416000 13.22144000 14.43480000 13.97456000\
13.30512000 16.31760000 13.97456000 10.20896000 3.80744000 -2.55224000 -6.31784000 -6.77808000 -4.01664000 -0.08368000\
1.75728000 3.80744000 1.92464000 0.62760000 -0.29288000 0.08368000 1.17152000 3.13800000 5.77392000 14.01640000\
9.83240000 12.80304000 15.94104000 15.48080000 14.97872000 17.61464000 14.81136000 7.07096000 0.41840000 -2.84512000\
...行C NH1 CT1 C NH1 1 24 24の意味は以下になります:
C NH1 CT1 C NH1: 主鎖C-N-CA-C, N-CA-C-Nに対するcmap1: 意味はあまりないcmapに対するidです.24 24: 2424のグリッドに分けていることを意味します
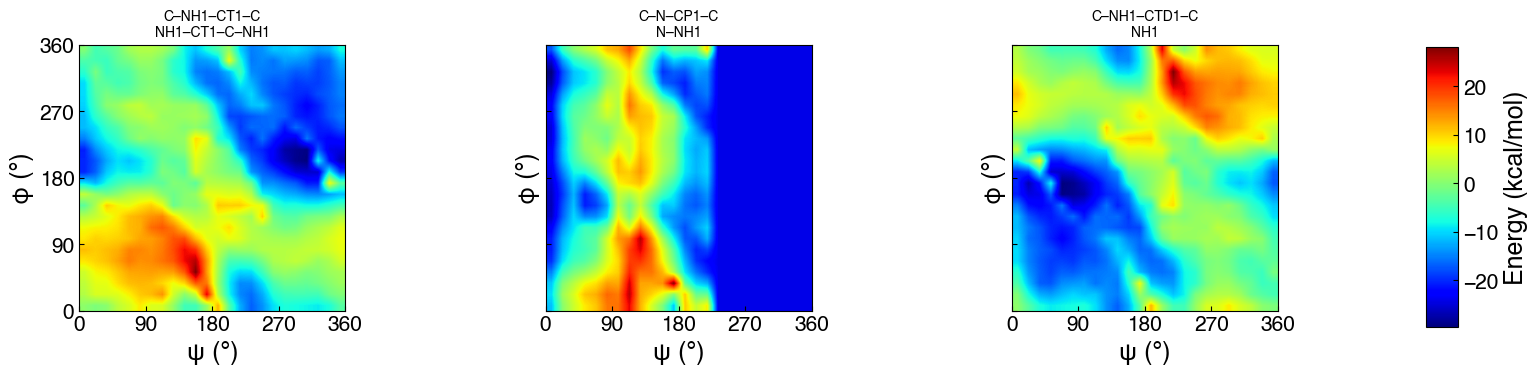
どのようなCMAPの情報がtopology fileに書かれているかを確認したjupyter notebookをここにおきました.結果の図(Figure 1 )だけ載せておきます.
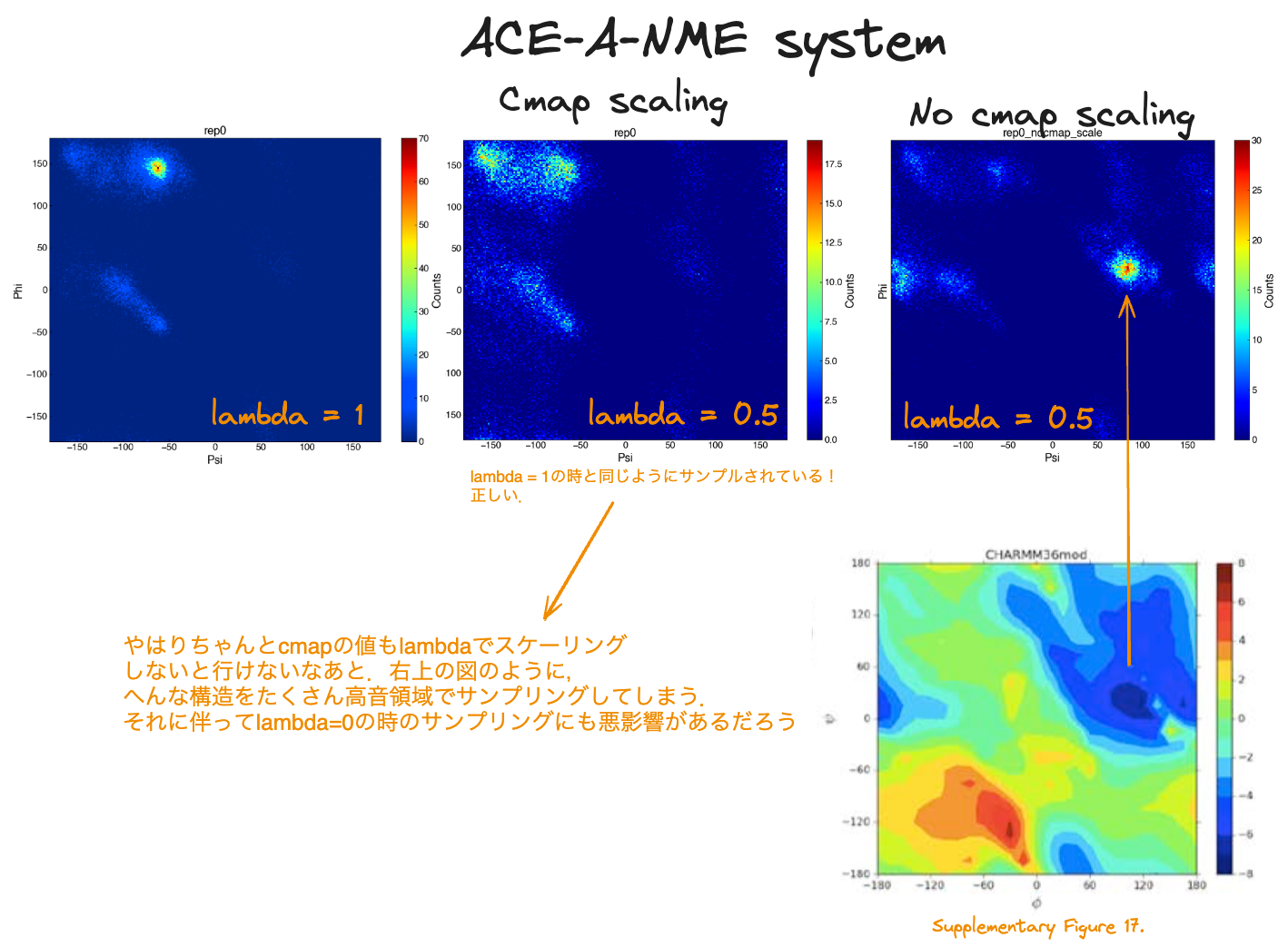
H-REMDにおけるCMAPに対するスケーリング
Hamiltonian-replica exchange MDをする際には,異なるレプリカ間のポテンシャルをスケーリングしますが,PLUMEDと呼ばれるソフトウェアでの実装では,デフォルト(2026-3時点)だとCMAPがスケーリングされません.なので,自前でトポロジーファイルをスケーリングするスクリプトを作成する必要があります.うまくスケーリングできているなら,以下のような図になるはずです:
References
- Huang, Jing, Rauscher, Sarah, Nawrocki, Grzegorz, Ran, Ting, Feig, Michael, de Groot, Bert L, Grubmüller, Helmut, MacKerell, Jr, Alexander D. "CHARMM36m: an improved force field for folded and intrinsically disordered proteins." Nat. Methods 2017, 14, (1), 71--73

 Google Scholar
Google Scholar Twitter
Twitter  DockerHub
DockerHub